Kleine Moleküle, wie Metaboliten, Ionen und Phytohormone treffen präzise Entscheidungen für die Pflanzenentwicklung. Mit unseren Augen können wir jedoch nicht sehen, wie solche Moleküle durch das Pflanzengewebe oder durch die Organe stolpern und tanzen. Auf dieser Seite wird kurz vorgestellt, wie wir das Unsichtbare sichtbar machen können.
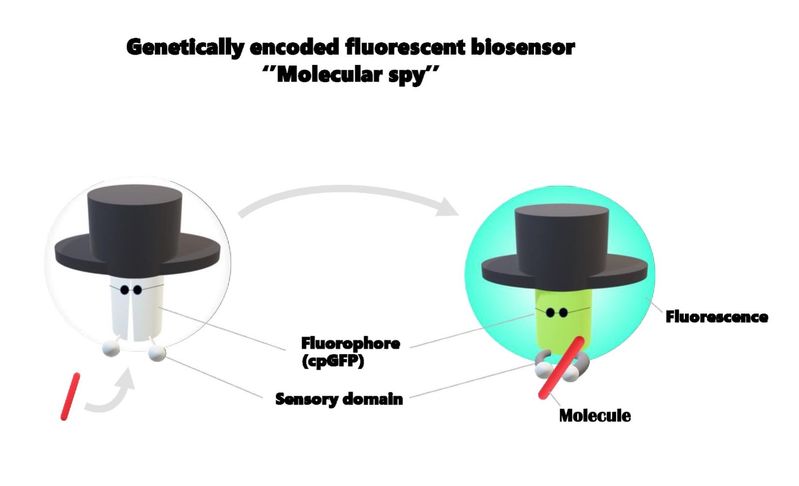
1961 entdeckte Osamu Shimomura unerwartet ein grün fluoreszierendes Protein (Green Fluorescence Protein, GFP) bei der Reinigung von Quallen und erhielt für seine Arbeit an diesem Protein den Nobelpreis für Chemie. Diese Entdeckung ermöglichte es den Wissenschaftler*innen, die verschiedenen biologischen Phänomene sichtbar zu machen. Da das Gen für GFP bekannt ist, sind wir derzeit in der Lage, das GFP mit einer typischen Transformationsmethode in die Pflanzenzelle einzuführen. Allerdings kann GFP die kleinen Moleküle nicht selbst erkennen. Wir müssen also das richtige Modul einsetzen, um den gewünschten Stoff zu erkennen, die so genannte sensorische Domäne.
Um die Anzahl der Moleküle mit GFP zu erkennen, ist außerdem eine Intensitätsänderung der Fluoreszenz erforderlich, wenn der Analyt von der sensorischen Domäne wahrgenommen wird. Eine der bekannten Technologien, um diese Intensitätsänderung der Fluoreszenz zu induzieren, ist "circularly permuted GFP (cpGFP)". Da das cpGFP-Protein in seiner dreidimensionalen Struktur (Konformation) relativ schwach gefaltet ist, induziert die Bindung der sensorischen Domäne an einen Analyten eine Konformationsänderung, gefolgt von der Intensitätsänderung der cpGFP-Fluoreszenz. Durch die genetische Fusion von cpGFP und der sensorischen Domäne sind wir also in der Lage, Biosensoren herzustellen, und dieser genetisch kodierte fluoreszierende Biosensor kann uns die Häufigkeit eines Moleküls eines bestimmten Analyten in der Zelle mitteilen.
Einer der Pioniere auf dem Gebiet der Biosensoren, Roger Tsien, sagte einmal, dass ''unsere Arbeit oft als Bau und Training von molekularen Spionen beschrieben wird, also Molekülen, die in eine Zelle oder einen Organismus eindringen und uns zurückmelden, wie die Bedingungen sind''. So wird der genetisch kodierte Sensor oft mit dem ''molekularen Spion'' verglichen. Aber was bedeutet ''molekularer Spion''?
Ich stelle mir vor, dass ein echter Spion die Verteidigung des Feindes unterwandern und die wertvollen Informationen melden muss. Als faszinierender molekularer Spion braucht ein Biosensor also eine große Fluoreszenzänderung vor und nach dem Erfassen des gewünschten Stoffes, die sogenannte ''Sensitivität''. Eine hohe Empfindlichkeit führt zu einer robusten Bildgebung mit geringem Rauschen. Der Kalzium-Biosensor zum Beispiel besitzt eine hohe Sensitivität und zeigt eine robuste Bildgebung zur Visualisierung der Kalziumdiffusion bei Blattverletzungen und zum Beispiel als Reaktion auf Berührung im Fall der Venusfliegenfalle.
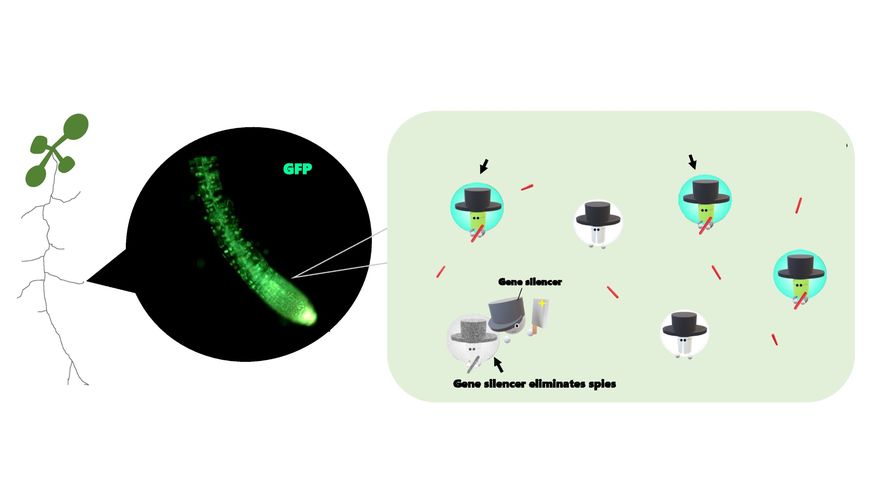
Andererseits, was ist der Feind des Biosensors innerhalb einer Pflanze? Es scheint, dass der "Gen-Silencer" nach molekularen Spionen Ausschau hält, um sie zu beseitigen. Bis jetzt haben mehrere Arbeiten darauf hingewiesen, dass eine hohe Häufigkeit von Sensoren zu einem Gen-Silencing-Effekt führt. Daher ist eine Strategie, die Häufigkeit von Biosensoren in der Pflanze auf einem Minimum zu halten. Eine andere Möglichkeit ist, Gen-Silencing-Mutanten zu verwenden, so dass wir den Gen-Silencing-Effekt ignorieren können.
In meinem CEPLAS-Projekt möchte ich mit Hilfe der "Matrjoschka-Technologie" einen faszinierenden molekularen Spion entwickeln, der eine hohe Empfindlichkeit und eine hohe Genauigkeit besitzt. Bei dieser Technologie werden mehrere fluoreszierende Proteine verwendet, die genetisch in nur einem Abschnitt kodiert sind; das Konzept erinnert an die verschachtelten russischen "Matrjoschka"-Puppen. Diese faszinierenden Sensoren haben potentiell gute Eigenschaften, um den molekularen Transportmechanismus während der Pflanzenentwicklung zu adressieren. Gute Sensoren wären in der Lage, uns völlig neue, unerwartete Einblicke in die molekularen Mechanismen der Pflanze zu geben.
Der originale Text ist in englischer Sprache und wurde für die deutsche Version übersetzt.
Planter’s Punch
Unter der Rubrik Planter’s Punch wird jeden Monat ein bestimmter Aspekt des CEPLAS Forschungsprogramms vorgestellt. Alle Beiträge werden von Mitgliedern der Graduiertenschule und des Postdoc Programms erstellt.
Zum Nachlesen
Isoda R, Yoshinari A, Ishikawa Y, Sadoine M, Simon R, Frommer WB, Nakamura M (2020) Sensors for the quantification, localization and analysis of the dynamics of plant hormones. Plant J.
Über den Autor

Yuuma Ishikawa ist Postdoc am Institut für Molekulare Physiologie der Heinrich-Heine-Universität Düsseldorf und seit Oktober 2020 Mitglied bei CEPLAS. Er absolvierte an der Saitama Universität in Japan den Studiengang Naturwissenschaften und Technik und erhielt den akademischen Grad „Doktor der Ingenieurwissenschaften“. Bevor er zu CEPLAS kam, lernte er bei INRA in Frankreich und war Mitglied der Frommer-Gruppe an der Nagoya-Universität in Japan.